Introducere
Rețelele Random Vector Functional Link (RVFL) oferă o alternativă simplă, dar puternică, la rețelele neuronale tradiționale pentru date tabulare. În loc să învețe straturi ascunse prin backpropagation, RVFL le generează la întâmplare (sau nu, dacă se utilizează o secvență deterministă de numere cvasialeatoare) și concentrează tot efortul de învățare pe un model liniar final, regularizat.
Formal, să
(X in mathbb{R}^{n times p})
fie datele de intrare. Rețelele RVFL (cele descrise în această postare pe blog) construiesc un set de caracteristici neliniare prin proiectarea (X) pe o matrice aleatorie
(W in mathbb{R}^{p times m},)
și aplicarea unei funcții de activare ((g(cdot))):
(H = gleft( frac{X – mu}{sigma} ; W right).)
Aceste caracteristici neliniare aleatorii sunt apoi concatenate cu intrările originale pentru a forma o matrice de proiectare augmentată:
(Z = (X | H).)
Predicția modelului este obținută prin potrivirea unui model liniar pe acest spațiu extins (deci, un GLM neliniar):
(hat{y} = Z beta.)
Deoarece (Z) poate fi de dimensiuni înalte și extrem de redundante, rețelele RVFL (cele descrise în această postare de blog) se bazează pe Regularizare Elastic Net (glmnet) pentru a estima coeficienții:
(hat{beta} = argmin_{beta}mathcal{L}(y, Zbeta) + lambda left(alpha ||beta||_1 + (1-alpha)||beta||_2^2right).)
În acest cadru, aleatorietatea creează un grup bogat de transformări neliniare, în timp ce regularizarea le selectează și le stabilizează pe cele mai utile. Rezultatul este un model neliniar care combină flexibilitatea rețelelor neuronale cu eficiența și robustețea metodelor liniare.
Desigur, această postare pe blog nu este o dovadă a titlului. Este vorba despre pachetul R rvflnet. Dar poți aprecia performanță ridicată a RVFL-urilor pe regresie, clasificare și analiza supraviețuirii, și în special pe cele controversate Boston set de date (funcționează la egalitate cu Random Forest sau Gradient Boosting).
0 – Instalați pachetul
install.packages("survival", repos = "https://cran.r-project.org") # survival analysis
install.packages("remotes", repos = "https://cran.r-project.org")
devtools::install_github('thierrymoudiki/rvflnet') # Nonlinear glm (RVFL networks)
1 – Regresie
set.seed(123)
library(glmnet)
data(Boston, package = "MASS")
# -------------------------
# Data
# -------------------------
X <- as.matrix(Boston(, -14))
y <- Boston$medv
n <- nrow(X)
idx <- sample(1:n, size = round(0.8 * n))
X_train <- X(idx, )
y_train <- y(idx)
X_test <- X(-idx, )
y_test <- y(-idx)
# -------------------------
# Grid
# -------------------------
grid <- expand.grid(
n_hidden = c(175, 200, 225, 250),
alpha = seq(0.1, 0.5, by=0.2),
include_original = c(TRUE, FALSE),
seed = 1,
stringsAsFactors = FALSE
)
results <- vector("list", nrow(grid))
# -------------------------
# Loop
# -------------------------
for (i in seq_len(nrow(grid))) {
params <- grid(i, )
#cat("n========================================n")
#cat(sprintf("Run %d / %dn", i, nrow(grid)))
#print(params)
# -------------------------
# Fit model
# -------------------------
fit <- rvflnet::rvflnet(
X_train, y_train,
n_hidden = params$n_hidden,
activation = "sigmoid",
W_type = "gaussian",
seed = params$seed,
include_original = params$include_original, # direct link, skip connection or not
alpha = params$alpha
)
# -------------------------
# Evaluate full lambda path
# -------------------------
lambdas <- fit$fit$lambda
preds <- predict(fit, newx = X_test, s = lambdas)
rmse_path <- sqrt(colMeans((preds - y_test)^2))
best_idx <- which.min(rmse_path)
best_rmse <- rmse_path(best_idx)
best_lambda <- lambdas(best_idx)
# -------------------------
# Sparsity
# -------------------------
coef_mat <- coef(fit, s = best_lambda)
nonzero <- sum(coef_mat(-1, 1) != 0)
# -------------------------
# Verbose output
# -------------------------
#cat(sprintf("Best RMSE: %.4fn", best_rmse))
#cat(sprintf("Best lambda: %.6fn", best_lambda))
#cat(sprintf("Non-zero coeffs: %dn", nonzero))
# -------------------------
# Store
# -------------------------
results((i)) <- data.frame(
n_hidden = params$n_hidden,
alpha = params$alpha,
include_original = params$include_original,
seed = params$seed,
rmse = best_rmse,
lambda = best_lambda,
nonzero = nonzero
)
}
# -------------------------
# Aggregate
# -------------------------
results_df <- do.call(rbind, results)
results_df <- results_df(order(results_df$rmse), )
print(head(results_df))
Loading required package: Matrix
Loaded glmnet 4.1-10
n_hidden alpha include_original seed rmse lambda nonzero
s= 0.027561759 200 0.1 TRUE 1 2.881935 0.02756176 190
s= 0.017620327 200 0.3 TRUE 1 2.884739 0.01762033 167
s= 0.012734248 200 0.5 TRUE 1 2.889339 0.01273425 158
s= 0.036435024 175 0.1 TRUE 1 2.920012 0.03643502 165
s= 0.016833926 175 0.5 TRUE 1 2.938472 0.01683393 136
s= 0.023293035 175 0.3 TRUE 1 2.941267 0.02329304 144
Un RMSE de 2,88 este la egalitate cu Random Forest sau Gradient Boosting, cu a semnificativ timp de calcul mai rapid.
2 – Clasificare
2 – 1 Clasificare binară
set.seed(123)
data(iris)
# Binary classification: setosa vs others
y <- ifelse(iris$Species == "setosa", 1, 0)
X <- as.matrix(iris(, 1:4))
# Train/test split
n <- nrow(X)
idx <- sample(1:n, size = round(0.8 * n))
X_train <- X(idx, )
y_train <- y(idx)
X_test <- X(-idx, )
y_test <- y(-idx)
# -------------------------
# Fit model
# -------------------------
cv_model <- rvflnet::cv.rvflnet(
X_train, y_train,
n_hidden = 50,
activation = "relu",
W_type = "gaussian",
family = "binomial",
nfolds = 5
)
# -------------------------
# Predictions (probabilities)
# -------------------------
(probs <- predict(cv_model, X_test, type = "response"))
# Convert to class
y_pred <- ifelse(probs > 0.5, 1, 0)
all.equal(as.numeric(y_pred), as.numeric(predict(cv_model, X_test, type="class")))
# -------------------------
# Diagnostics
# -------------------------
# Accuracy
acc <- mean(drop(y_pred) == y_test)
cat("Accuracy:", acc, "n")
# Confusion matrix
table(Predicted = y_pred, Actual = y_test)
| lambda.min |
|---|
| 0,9997617002 |
| 0,9992267955 |
| 0,9997120678 |
| 0,9997524867 |
| 0,9996600481 |
| 0,9992472082 |
| 0,9996101744 |
| 0,9999356520 |
| 0,9998139568 |
| 0,9995418762 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0019937012 |
| 0,0003328885 |
| 0,0005459970 |
| 0,0003328885 |
| 0,0005035848 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
| 0,0003328885 |
ADEVĂRAT
Accuracy: 1
Actual
Predicted 0 1
0 20 0
1 0 10
2 – 2 Clasificare multiclasă
set.seed(123)
data(iris)
y <- as.numeric(iris$Species)
X <- as.matrix(iris(, 1:4))
# Train/test split
n <- nrow(X)
idx <- sample(1:n, size = round(0.8 * n))
X_train <- X(idx, )
y_train <- y(idx)
X_test <- X(-idx, )
y_test <- y(-idx)
# -------------------------
# Fit model
# -------------------------
cv_model <- rvflnet::rvflnet(
X_train, y_train,
n_hidden = 50,
activation = "relu",
W_type = "gaussian",
family = "multinomial",
nlambda = 25,
nfolds = 5
)
# -------------------------
# Diagnostics
# -------------------------
# Accuracy
acc <- colMeans(predict(cv_model, X_test, type="class") == y_test)
cat("Accuracies:", acc, "n") # consider other metrics
Accuracies: 0.1666667 0.7666667 0.9333333 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667 0.9666667
3 – Analiza neliniară a supraviețuirii Cox
3 – 1 Exemplul 1
library(survival)
library(rvflnet)
data(ovarian)
X <- as.matrix(ovarian(, c("age", "resid.ds", "rx", "ecog.ps")))
y <- Surv(ovarian$futime, ovarian$fustat)
set.seed(123)
n <- nrow(X)
train_idx <- sample(1:n, size = round(0.8 * n))
X_train <- X(train_idx, )
X_test <- X(-train_idx, )
y_train <- y(train_idx)
y_test <- y(-train_idx)
# -------------------------
# Fit model
# -------------------------
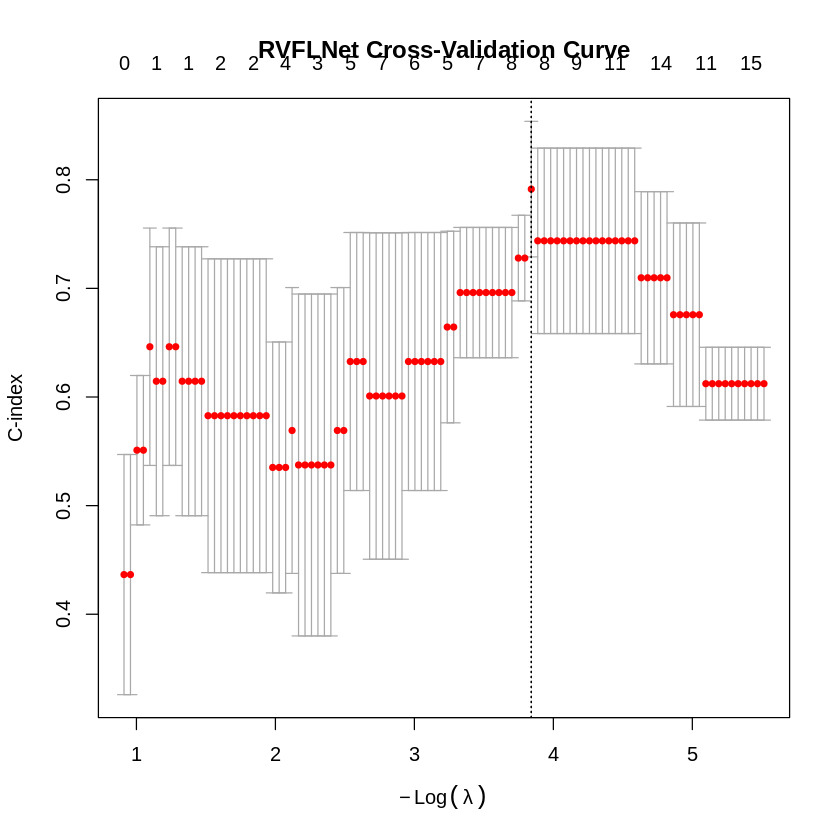
cv_fit <- rvflnet::cv.rvflnet(
X_train, y_train,
family = "cox",
nfolds = 5,
type.measure = "C"
)
plot(cv_fit)
# Out-of-sample C-index
print(glmnet::Cindex(pred = predict(cv_fit, X_test), y = y_test))
Warning message in data(ovarian):
“data set ‘ovarian’ not found”
(1) 0.8571429
3 – 2 Exemplul 2
library(glmnet)
library(survival)
data(pbc)
pbc2 <- pbc(!is.na(pbc$trt), )
pbc2$event <- as.integer(pbc$status(!is.na(pbc$trt)) == 2)
pbc2$sex_n <- as.integer(pbc2$sex == "f")
feat_cols <- c("trt","age","sex_n","ascites","hepato","spiders","edema",
"bili","chol","albumin","copper","alk.phos","ast",
"trig","platelet","protime","stage")
df <- pbc2(, c("time", "event", feat_cols))
for (col in feat_cols)
if (any(is.na(df((col)))))
df((col))(is.na(df((col)))) <- median(df((col)), na.rm = TRUE)
set.seed(42)
idx_train <- sample(nrow(df), floor(0.75 * nrow(df)))
train <- df(idx_train, ); test <- df(-idx_train, )
X_tr <- as.matrix(train(, feat_cols))
X_te <- as.matrix(test(, feat_cols))
y_tr <- Surv(train$time, train$event)
fit <- rvflnet::rvflnet(
X_tr, y_tr,
family = "cox",
alpha=0.1, lambda=0.1 # not recommended
)
y_te <- Surv(test$time, test$event)
ci <- glmnet::Cindex(predict(fit, X_te), y_te)
cat("n=== Test-set C-index ===n")
print(ci)
=== Test-set C-index ===
(1) 0.8218117
fit <- rvflnet::rvflnet(
X_tr, y_tr,
family = "cox",
alpha=0.1, nlambda=50
)
y_te <- Surv(test$time, test$event)
(cis <- apply(predict(fit, X_te), 2, function(x) glmnet::Cindex(x, y_te)))
#cat("n=== Test-set C-index ===n")
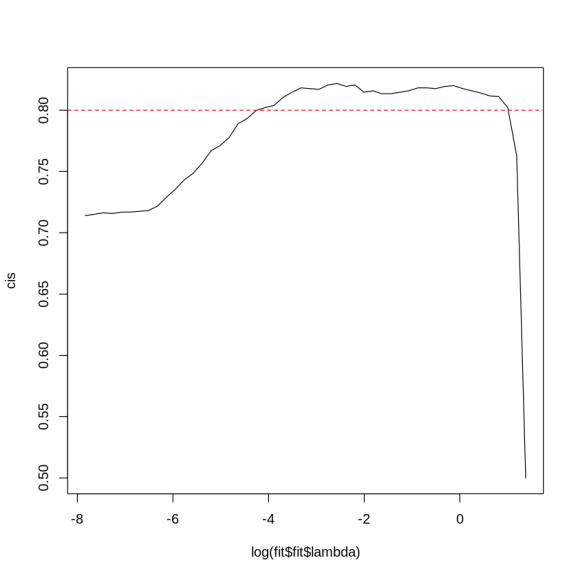
plot(log(fit$fit$lambda), cis, type="l")
abline(h=0.8, lty=2, col="red")
- s0
- 0,5
- s1
- 0,762812872467223
- s2
- 0,802145411203814
- s3
- 0,811084624553039
- s4
- 0,811680572109654
- s5
- 0,814064362336114
- s6
- 0,815852205005959
- s7
- 0,817640047675805
- s8
- 0,820023837902265
- s9
- 0,81942789034565
- s10
- 0,817640047675805
- s11
- 0,81823599523242
- s12
- 0,81823599523242
- s13
- 0,815852205005959
- s14
- 0,814660309892729
- s15
- 0,813468414779499
- s16
- 0,813468414779499
- s17
- 0,815852205005959
- s18
- 0,814660309892729
- s19
- 0,82061978545888
- s20
- 0,81942789034565
- s21
- 0,82181168057211
- s22
- 0,82061978545888
- s23
- 0,817044100119189
- s24
- 0,817640047675805
- s25
- 0,81823599523242
- s26
- 0,814660309892729
- s27
- 0,810488676996424
- s28
- 0,803933253873659
- s29
- 0,802145411203814
- s30
- 0,799761620977354
- s31
- 0,793206197854589
- s32
- 0,789034564958284
- s33
- 0,777711561382598
- s34
- 0,771156138259833
- s35
- 0,766984505363528
- s36
- 0,756853396901073
- s37
- 0,748510131108462
- s38
- 0,743146603098927
- s39
- 0,735399284862932
- s40
- 0,728843861740167
- s41
- 0,721692491060787
- s42
- 0,718116805721096
- s43
- 0,717520858164482
- s44
- 0,716924910607867
- s45
- 0,716924910607867
- s46
- 0,715733015494636
- s47
- 0,716328963051251
- s48
- 0,715137067938021
- s49
- 0,713945172824791