(Acest articol a fost publicat pentru prima dată pe R – Myscapeși cu amabilitate a contribuit la R-bloggeri). (Puteți raporta problema legată de conținutul acestei pagini aici)
Doriți să vă distribuiți conținutul pe R-bloggeri? dați clic aici dacă aveți un blog, sau aici dacă nu aveți.
Prezentare generală
Analiza expresiei diferențiale (DE) este utilizată pentru a identifica genele care conduc modelele de variație asociate cu grupuri de probe.
Este ușor să faci liste de gene DE folosind aplicația freeCount DA.
Obiectivele de învățare
- Să poată efectua comparații pentru a identifica genele DE cu edgeR
- Fiți confortabil cu setarea pragurilor FDR și LFC pentru a filtra rezultatele DE
- Aflați cum să pregătiți rezultatele DE pentru analiza în aval (operații funcționale, de rețea, set)
muchieR
Pachetul R muchieR utilizează media tăiată a valorilor M (TMM) pentru normalizare înainte de analiza DE cu distribuții binomiale negative.
Datele sunt normalizat pentru a lua în considerare diferențele de dimensiune a eșantionului și variația dintre eșantioane.
Datele de numărare normalizate sunt apoi utilizate pentru a estima per-genă modificările de ori și efectuați analiza DE.
Înainte de a începe
Exercițiul din acest tutorial va folosi aplicațiile freeCount din RStudio pe un computer personal. Asigurați-vă că aveți instrumentele care urmează descărcate și instalat și la zi pe computerul personal:
- Mediul software R
- Aplicația desktop RStudio
Pentru utilizatorii de Windows, instalați suplimentar RTools.
De asemenea, este posibil să rulați online aplicațiile freeCount prin Posit Cloud. Pentru a vedea cum, consultați tutorialul freeCount Bioinformatics Analysis Apps on Posit Cloud.
Date de intrare
- Descărcați fișierul tribolium counts
- Descărcați fișierul de design tribolium
Sfat! Faceți clic dreapta și selectați Salvați ca… pentru a descărca fișierele de mai sus în format csv.
Exemplu de date
În această lecție vom folosi date dintr-un studiu al efectelor radiațiilor ultraviolete (UVR) asupra larvelor gândacului roșu de făină intitulat „Digital gene expression profile in larve of Tribolium castaneum la diferite perioade post expunerea la UV-B“.


UVR este comun în multe medii și variază foarte mult în intensitatea și compoziția sa, cum ar fi diferitele rapoarte ale radiației UV-A și UV-B. Diferitele forme de UVR au efecte distincte și frecvent dăunătoare asupra organismelor și sistemelor biologice.
Studiu Design
Există doi factori pentru fiecare eșantion și în cadrul fiecăruia dintre acești factori sunt două niveluri:
- The stare factorul are nivelurile de cntrl şi trata
- The timp factorul are nivelurile de 4h şi 24h
Suntem capabili să ne grupăm datele folosind diferitele niveluri ale fiecărui factor, apoi putem compara nivelurile de expresie ale genelor din acele grupuri pentru a identifica DE.


Porniți aplicația de analiză
Următorii pași vă arată cum să obțineți și să începeți să rulați aplicația de analiză a expresiei diferențiale (DA) freeCount.
- Descărcați gratuit aplicațiile Count R Shiny
- Accesați https://github.com/ElizabethBrooks/freeCount
- Faceți clic pe verde < > Cod buton
- Clic Descărcați ZIP
- Extrageți freeCount-principal director
- Navigați la aplicații director
- Deschideți DA.R fișier în RStudio
- Clic Instala pe bannerul galben pentru a instala pachetele R necesare (sau rulați codul pe rândurile de la 10 la 19)
- Faceți clic pe Rulați aplicația butonul din colțul din dreapta sus al panoului sursă
Procesul de analiză
Efectuați următorii pași pentru a face o listă de gene DE care pot fi apoi utilizate într-o analiză în aval (de exemplu, funcționale).
- Încărcați datele și faceți clic Executați analiza
- Examinați setările inițiale de pe Analiză fila
- Selectați grupurile de eșantion pentru a compara și faceți clic Analiza
- Explorați datele filtrate și normalizate pe Normalizarea datelor fila
- Inspectați modelele de variație între eșantioane afișate în diagramele de grupare de pe Explorarea datelor fila
- Inspectați rezultatele analizei DE și numărul de gene DE pe Rezultate fila
- Comparați grupările de probe din harta termică a genelor DE cu diagramele de grupare
- Ajustați setările FDR și LFC pentru a filtra rezultatele genei DE
- Creați o listă organizată de gene DE repetând pașii de la 6 la 8
- Descărcați lista curată a genelor DE
Încărcați datele
Încărcați datele și faceți clic Executați analiza.


Examinați setările inițiale
Examinați setările inițiale de pe Analiză fila.


Selectați o comparație
Selectați grupurile de eșantion pentru a compara și faceți clic Analiza.


Explorați datele filtrate și normalizate
Explorați datele filtrate și normalizate de pe Normalizarea datelor fila.


Analiza rețelei în aval
Pentru analiza rețelei în aval, faceți clic pe Descărcați tabelul butonul pentru a descărca Tabelul de numărare a genelor normalizate. Acest tabel poate fi introdus în aplicația freeCount NA împreună cu un fișier de proiectare a studiului.
Inspectați modelele de variație
Inspectați modelele de variație între eșantioane afișate în diagramele de grupare de pe Explorarea datelor fila.

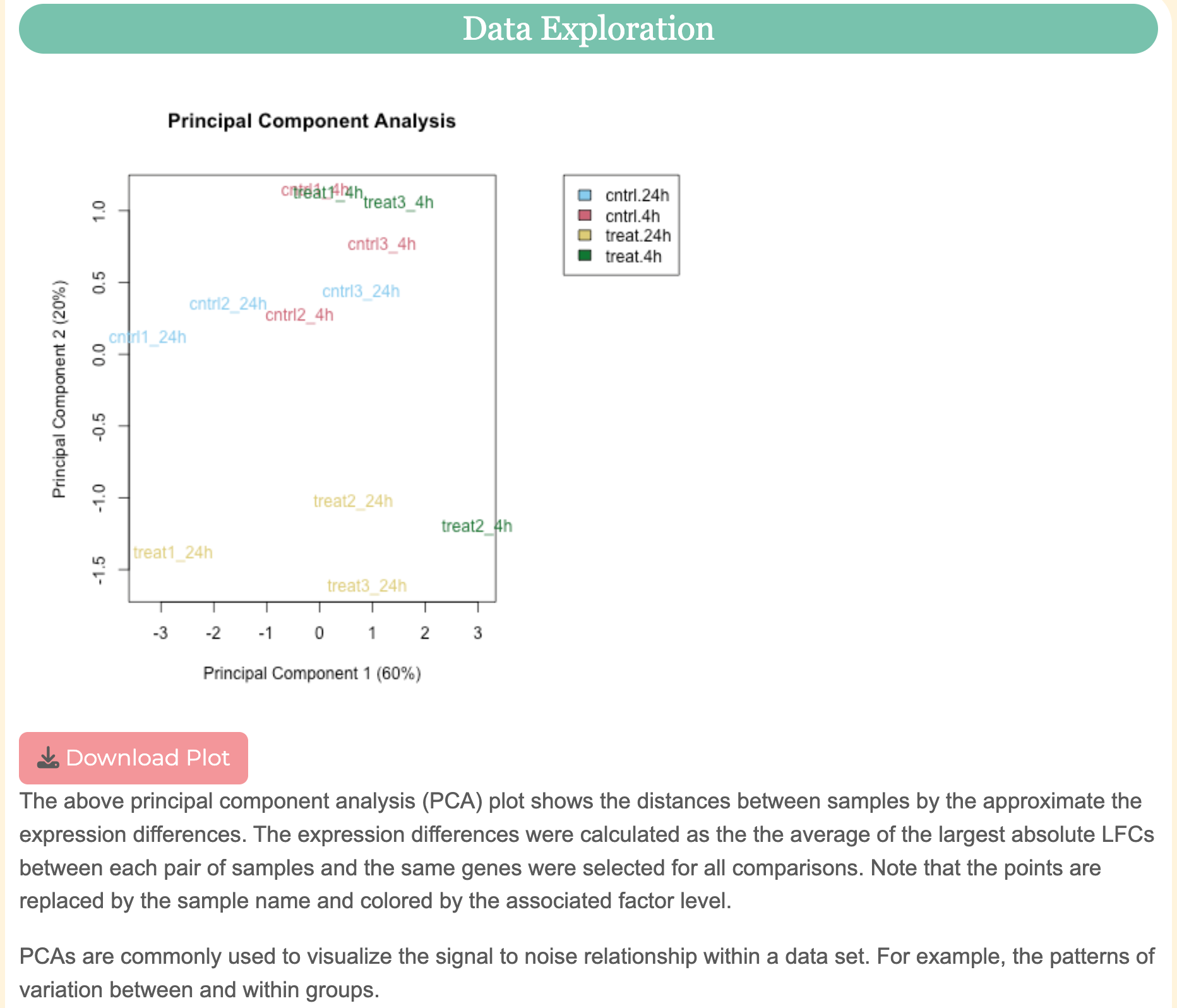
Observați în PCA de mai sus că câteva mostre din diferite grupuri sunt amestecate și grupate cu alte grupuri. De exemplu, o probă din grupul treat.4h (treat2_4h) nu este grupată cu celelalte probe din acel grup.
Modelele de variație între eșantioane pe care le observăm aici ne arată la ce să ne așteptăm atunci când analizăm setul rezultat de gene DE. Aceste modele ne vor ajuta să ne ghidăm în timp ce setăm pragurile FDR și LFC pentru a ne filtra rezultatele.
Inspectați rezultatele analizei DE
Inspectați rezultatele analizei DE și numărul de gene DE pe Rezultate fila.


Comparați grupările de mostre
Comparați grupările de probe din harta termică a genelor DE (Rezultate fila) la diagramele de grupare (Explorarea datelor fila).


Ajustați setările FDR și LFC
Ajustați setările FDR și LFC pentru a filtra rezultatele genei DE.


Filtrarea rezultatelor analizei DE
Regla praguri de…
- Creșterea LFC în date zgomotoase să aibă diferențe mai sigure
- Scăderea FDR să se concentreze asupra ținte cu probabilitate ridicată
Reduceți rezultatele la genele despre care credeți că conduc modelele de variație observate în diagramele de grupare.
Verificați FDR şi LFC pragurile prin vizualizarea tiparelor doar cu acele gene.
Verificați setările de analiză
Verificați dacă setările de analiză s-au actualizat uitându-vă la Setări curente de analiză în partea stângă a aplicației.


Creați o listă curată de gene DE
Creați o listă organizată de gene DE repetând pașii de la 6 la 8.
Poate fi necesar să ajustați în mod repetat setările și să inspectați rezultatele genei DE pentru a crea o listă bine îngrijită și gestionabilă de gene DE.
Descărcați lista DE Gene
În cele din urmă, descărcați lista curată a genelor DE.


The Tabelul rezultatelor analizei DE poate fi utilizat în analiza funcțională din aval. Acest tabel poate fi introdus în aplicația freeCount FA împreună cu un fișier de adnotări.
The Tabel cu rezultate semnificative ale analizei DE poate fi utilizat cu operațiuni de set pentru a identifica seturi de gene partajate sau unice. Acest tabel poate fi introdus în aplicația freeCount SO împreună cu alte liste de gene DE dintr-un experiment.
