(Acest articol a fost publicat pentru prima dată pe R – Myscapeși cu amabilitate a contribuit la R-bloggeri). (Puteți raporta problema legată de conținutul acestei pagini aici)
Doriți să vă distribuiți conținutul pe R-bloggeri? dați clic aici dacă aveți un blog, sau aici dacă nu aveți.
Prezentare generală
Analiza rețelei de co-expresie genetică ponderată (WGCNA) este utilizată pentru a investiga funcția genelor la nivel de sistem. Într-o analiză de rețea, genele cu modele similare de expresie sunt grupate împreună în module. Seturile de gene din aceste module sunt co-exprimate ca rezultat al funcțiilor biologice comune, căilor, țesuturilor, trăsăturilor etc.
Ce gene împărtășesc modele de expresie între mostre?
Aplicația freeCount NA vă va ajuta să efectuați analize de rețea a numărului de gene normalizate, care pot fi produse din instrumente de analiză a expresiei diferențiale precum freeCount DA.
Obiectivele de învățare
- Aflați cum să faceți liste de gene co-exprimate conținute în modulele de rețea
- Exersați ajustarea setărilor pentru a construi rețele de co-expresie genetică
- Înțelegeți cum să identificați seturi de gene care împărtășesc funcții la nivel de sistem
Înrudit
Acest tutorial este al treilea dintr-o serie și folosește datele normalizate TMM realizate în tutorialul Making DE Gene Lists with freeCount.
WGCNA
Construirea rețelelor de co-expresie folosind pachetul WGCNA R este un proces complicat, dar conceptual simplu (DOI: 10.2202/1544-6115.1128). Într-o rețea de co-expresie nodurile reprezintă gene. Nodurile sunt conectate dacă genele corespunzătoare sunt co-exprimate semnificativ în probe alese corespunzător.
Având în vedere ipotezele WGCNA, este important să vă proiectați studiul în mod corespunzător pentru analiza rețelei, astfel încât să puteți trage concluzii rezonabile din rezultate. În primul rând, WGCNA presupune că datele de numărare au fost preprocesate și normalizate (DOI: 10.1186/1471-2105-9-559). De asemenea, este important să luați în considerare dacă aveți suficiente mostre pentru a construi o rețea informativă, în care semnalul de co-exprimare nu este influențat de un anumit eșantion.
Înainte de a începe
Exercițiul din acest tutorial va folosi aplicațiile freeCount din RStudio pe un computer personal. Asigurați-vă că aveți următoarele instrumente descărcate, instalate și la zi pe computerul personal:
- Mediul software R
- Aplicația desktop RStudio
Pentru utilizatorii de Windows, instalați suplimentar RTools.
Ea nu este este posibil să rulați aplicația freeCount NA online prin intermediul plan gratuit de Posit Cloud, deoarece necesită prea multă memorie.
Date de intrare
- Descărcați fișierul de numărări normalizate tribolium
- Descărcați fișierul de design experimental tribolium
Sfat! Faceți clic dreapta și selectați Salvați ca… pentru a descărca fișierele de mai sus în formatele necesare.
Aplicația de analiză
Următorii pași vă arată cum să obțineți și să începeți să rulați aplicația de analiză a rețelei (NA) freeCount.
- Descărcați gratuit aplicațiile Count R Shiny
- Accesați https://github.com/ElizabethBrooks/freeCount
- Faceți clic pe verde < > Cod buton
- Clic Descărcați ZIP
- Extrageți freeCount-principal director
- Navigați la aplicații director
- Deschideți NA.R fișier în RStudio
- Clic Instala pe bannerul galben pentru a instala pachetele R necesare (sau rulați codul pe rândurile de la 10 la 20)
- Faceți clic pe Rulați aplicația butonul din colțul din dreapta sus al panoului sursă
Procesul de analiză
Efectuați următorii pași pentru a face liste de gene co-exprimate conținute în modulele de rețea.
- Încărcați datele și faceți clic Încărcați
- Faceți clic pe Executați analiza butonul care apare în partea stângă a ecranului
- Examinați setările de date de pe Curățarea datelor fila
- Ajustați setările de rețea pe Construcția rețelei fila
- Creați o rețea informativă și o listă organizată de gene co-exprimate repetând pașii 3 și 4
- Descărcați liste de gene sau module proprii din Rezultate fila
1. Încărcați date
Încărcați datele și faceți clic Încărcați.


Date de intrare
- Primul fișier pe care trebuie să îl încărcați este tabelul numărului de gene care are numărul de gene normalizate pentru experimentul tău. În acest tutorial, folosim fișierul de numărări normalizate tribolium.
- Al doilea fișier pe care trebuie să îl încărcați este tabel cu proiectul experimental care descrie mostrele din studiul dumneavoastră. În acest tutorial, folosim fișierul de design experimental tribolium.
2. Executați analiza
Faceți clic pe Executați analiza butonul care apare în partea stângă a ecranului.

3. Examinați setările datelor
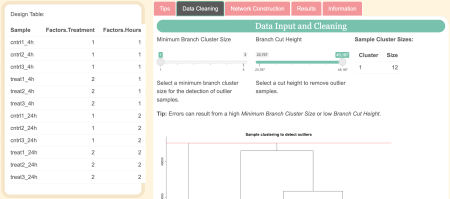
Examinați setările de date de pe Curățarea datelor fila.
The Dimensiunea minimă a grupului de ramuri şi Înălțimi de tăiere a ramurilor poate fi ajustat pentru a ajuta la identificarea și eliminarea valorii aberante din datele de intrare. După modificarea acestor setări, uitați-vă la cele ulterioare Gruparea probelor pentru a detecta valori aberante trasează pentru a vedea ce probe nu se grupează bine cu grupurile lor și ar putea fi necesar să fie eliminate. Linia roșie este înălțimea de tăiere care va fi folosită pentru a elimina valorile aberante.

4. Ajustați Setările de rețea
Ajustați setările suplimentare pe Construcția rețelei fila.
Schimbați Puterea de prag moale pentru a schimba intervalul de puteri de prag soft sugerate (numere roșii) în următoarele grafice. Soft Thresholding atribuie o greutate de conexiune fiecărei perechi de gene.

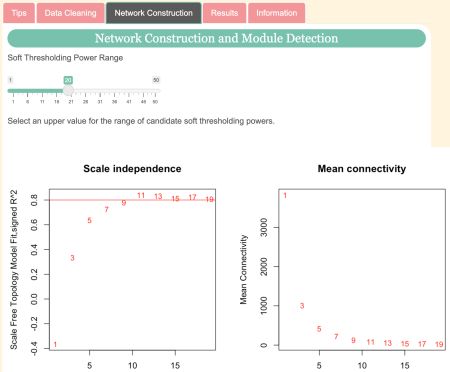
Apoi, setați Puterea de prag moale privind cele de mai sus Independența la scară trasează pentru a vedea unde se încadrează modelul de topologie fără scară recomandată (linia roșie a axei y). Observați ce număr roșu este cel mai apropiat de linia roșie de pe axa y. Apoi, uită-te la Conectivitate medie trasează pentru a vedea la ce corespunde acel număr în conectivitatea medie (axa y).

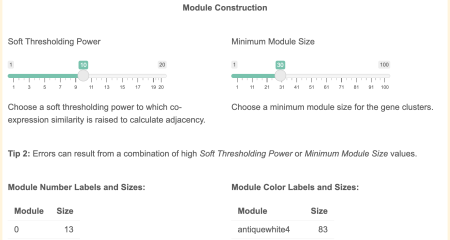
Apoi, puteți seta Modulul Eigegene Înălțime de tăiere în Construcția rețelei secțiune. Acest lucru va permite să ajustați dimensiunea modulelor dvs. prin îmbinarea modulelor în funcție de similitudinea co-expresiei.


5. Creați rezultate organizate
Creați o rețea informativă și o listă organizată de gene co-exprimate repetând pașii 3 și 4.
Poate fi necesar să ajustați în mod repetat setările și să inspectați rețeaua pentru a crea o listă bine îngrijită de gene de co-expresie grupate într-un set gestionabil de module.
6. Descărcați rezultatele
Descărcați liste de gene sau module proprii din Rezultate fila.


The Date despre modulul genelor tabelul conține lista de gene co-exprimate asociate cu diferite module de rețea. Acest fișier poate fi introdus în aplicația de analiză funcțională freeCount FA pentru a explora funcțiile potențiale ale setului de gene conținute în fiecare modul.
The Date de expresie proprie tabelul are datele de expresie proprii din modulele de rețea. Acest fișier poate fi utilizat în diferite analize în aval, cum ar fi o analiză diferențială a expresiei genelor proprii.
